Îmbunătățirea clasificării caracteristicilor cu nuclee cuantice proiectate
Estimare utilizare: 80 de minute pe un procesor Heron r3 (NOTĂ: Aceasta este doar o estimare. Timpul tău de execuție poate varia.)
În acest tutorial, demonstrăm cum să rulezi un nucleu cuantic proiectat (PQK) cu Qiskit pe un set de date biologice din lumea reală, bazat pe articolul Enhanced Prediction of CAR T-Cell Cytotoxicity with Quantum-Kernel Methods [1].
PQK este o metodă utilizată în învățarea automată cuantică (QML) pentru a codifica date clasice într-un spațiu de caracteristici cuantic și a le proiecta înapoi în domeniul clasic, folosind calculatoare cuantice pentru a îmbunătăți selecția caracteristicilor. Implică codificarea datelor clasice în stări cuantice cu ajutorul unui Circuit cuantic, de obicei printr-un proces numit mapare a caracteristicilor, în care datele sunt transformate într-un spațiu Hilbert de înaltă dimensionalitate. Aspectul „proiectat" se referă la extragerea informațiilor clasice din stările cuantice, prin măsurarea unor observabile specifice, pentru a construi o matrice nucleu care poate fi utilizată în algoritmi clasici bazați pe nucleu, cum ar fi mașinile cu vectori suport. Această abordare valorifică avantajele computaționale ale sistemelor cuantice pentru a obține potențial performanțe mai bune la anumite sarcini comparativ cu metodele clasice.
Acest tutorial presupune, de asemenea, o familiarizare generală cu metodele QML. Pentru o explorare mai aprofundată a QML, consultă cursul Quantum machine learning din IBM Quantum Learning.
Cerințe
Înainte de a începe acest tutorial, asigură-te că ai instalate următoarele:
- Qiskit SDK v2.0 sau mai recent, cu suport pentru vizualizare
- Qiskit Runtime v0.40 sau mai recent (
pip install qiskit-ibm-runtime) - Category encoders 2.8.1 (
pip install category-encoders) - NumPy 2.3.2 (
pip install numpy) - Pandas 2.3.2 (
pip install pandas) - Scikit-learn 1.7.1 (
pip install scikit-learn) - Tqdm 4.67.1 (
pip install tqdm)
Configurare
# Added by doQumentation — required packages for this notebook
!pip install -q category-encoders numpy pandas qiskit qiskit-ibm-runtime scipy scikit-learn tqdm
import warnings
# Standard libraries
import os
import numpy as np
import pandas as pd
# Machine learning and data processing
import category_encoders as ce
from scipy.linalg import inv, sqrtm
from sklearn.metrics.pairwise import rbf_kernel
from sklearn.model_selection import GridSearchCV, StratifiedKFold
from sklearn.svm import SVC
# Qiskit and Qiskit Runtime
from qiskit import QuantumCircuit
from qiskit.circuit import ParameterVector
from qiskit.circuit.library import UnitaryGate, ZZFeatureMap
from qiskit.quantum_info import SparsePauliOp, random_unitary
from qiskit.transpiler import generate_preset_pass_manager
from qiskit_ibm_runtime import (
Batch,
EstimatorOptions,
EstimatorV2 as Estimator,
QiskitRuntimeService,
)
# Progress bar
import tqdm
warnings.filterwarnings("ignore")
Pasul 1: Maparea intrărilor clasice la o problemă cuantică
Pregătirea setului de date
În acest tutorial folosim un set de date biologice din lumea reală pentru o sarcină de clasificare binară, generat de Daniels et al. (2022) și care poate fi descărcat din materialul suplimentar inclus în articol. Datele constau din celule CAR T, care sunt celule T modificate genetic utilizate în imunoterapie pentru tratarea anumitor tipuri de cancer. Celulele T, un tip de celule imune, sunt modificate în laborator pentru a exprima receptori antigenici chimerici (CARs) care vizează proteine specifice de pe celulele canceroase. Aceste celule T modificate pot recunoaște și distruge celulele canceroase mai eficient. Caracteristicile datelor sunt motivele celulelor CAR T, care se referă la componentele structurale sau funcționale specifice ale CAR-ului inginerat în celulele T. Pe baza acestor motive, sarcina noastră este să prezicem citotoxicitatea unei celule CAR T date, etichentând-o fie ca toxică, fie ca non-toxică. Cele de mai jos prezintă funcțiile auxiliare pentru preprocesarea acestui set de date.
def preprocess_data(dir_root, args):
"""
Preprocess the training and test data.
"""
# Read from the csv files
train_data = pd.read_csv(
os.path.join(dir_root, args["file_train_data"]),
encoding="unicode_escape",
sep=",",
)
test_data = pd.read_csv(
os.path.join(dir_root, args["file_test_data"]),
encoding="unicode_escape",
sep=",",
)
# Fix the last motif ID
train_data[train_data == 17] = 14
train_data.columns = [
"Cell Number",
"motif",
"motif.1",
"motif.2",
"motif.3",
"motif.4",
"Nalm 6 Cytotoxicity",
]
test_data[test_data == 17] = 14
test_data.columns = [
"Cell Number",
"motif",
"motif.1",
"motif.2",
"motif.3",
"motif.4",
"Nalm 6 Cytotoxicity",
]
# Adjust motif at the third position
if args["filter_for_spacer_motif_third_position"]:
train_data = train_data[
(train_data["motif.2"] == 14) | (train_data["motif.2"] == 0)
]
test_data = test_data[
(test_data["motif.2"] == 14) | (test_data["motif.2"] == 0)
]
train_data = train_data[
args["motifs_to_use"] + [args["label_name"], "Cell Number"]
]
test_data = test_data[
args["motifs_to_use"] + [args["label_name"], "Cell Number"]
]
# Adjust motif at the last position
if not args["allow_spacer_motif_last_position"]:
last_motif = args["motifs_to_use"][len(args["motifs_to_use"]) - 1]
train_data = train_data[
(train_data[last_motif] != 14) & (train_data[last_motif] != 0)
]
test_data = test_data[
(test_data[last_motif] != 14) & (test_data[last_motif] != 0)
]
# Get the labels
train_labels = np.array(train_data[args["label_name"]])
test_labels = np.array(test_data[args["label_name"]])
# For the classification task use the threshold to binarize labels
train_labels[train_labels > args["label_binarization_threshold"]] = 1
train_labels[train_labels < 1] = args["min_label_value"]
test_labels[test_labels > args["label_binarization_threshold"]] = 1
test_labels[test_labels < 1] = args["min_label_value"]
# Reduce data to just the motifs of interest
train_data = train_data[args["motifs_to_use"]]
test_data = test_data[args["motifs_to_use"]]
# Get the class and motif counts
min_class = np.min(np.unique(np.concatenate([train_data, test_data])))
max_class = np.max(np.unique(np.concatenate([train_data, test_data])))
num_class = max_class - min_class + 1
num_motifs = len(args["motifs_to_use"])
print(str(max_class) + ":" + str(min_class) + ":" + str(num_class))
train_data = train_data - min_class
test_data = test_data - min_class
return (
train_data,
test_data,
train_labels,
test_labels,
num_class,
num_motifs,
)
def data_encoder(args, train_data, test_data, num_class, num_motifs):
"""
Use one-hot or binary encoding for classical data representation.
"""
if args["encoder"] == "one-hot":
# Transform to one-hot encoding
train_data = np.eye(num_class)[train_data]
test_data = np.eye(num_class)[test_data]
train_data = train_data.reshape(
train_data.shape[0], train_data.shape[1] * train_data.shape[2]
)
test_data = test_data.reshape(
test_data.shape[0], test_data.shape[1] * test_data.shape[2]
)
elif args["encoder"] == "binary":
# Transform to binary encoding
encoder = ce.BinaryEncoder()
base_array = np.unique(np.concatenate([train_data, test_data]))
base = pd.DataFrame(base_array).astype("category")
base.columns = ["motif"]
for motif_name in args["motifs_to_use"][1:]:
base[motif_name] = base.loc[:, "motif"]
encoder.fit(base)
train_data = encoder.transform(train_data.astype("category"))
test_data = encoder.transform(test_data.astype("category"))
train_data = np.reshape(
train_data.values, (train_data.shape[0], num_motifs, -1)
)
test_data = np.reshape(
test_data.values, (test_data.shape[0], num_motifs, -1)
)
train_data = train_data.reshape(
train_data.shape[0], train_data.shape[1] * train_data.shape[2]
)
test_data = test_data.reshape(
test_data.shape[0], test_data.shape[1] * test_data.shape[2]
)
else:
raise ValueError("Invalid encoding type.")
return train_data, test_data
Poți rula acest tutorial executând celula de mai jos, care creează automat structura de foldere necesară și descarcă atât fișierele de antrenament, cât și cele de test direct în mediul tău. Dacă ai deja aceste fișiere local, acest pas le va suprascrie în siguranță pentru a asigura consistența versiunii.
## Download dataset
# Create data directory if it doesn't exist
!mkdir -p data_tutorial/pqk
# Download the training and test sets from the official Qiskit documentation repo
!wget -q --show-progress -O data_tutorial/pqk/train_data.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/train_data.csv
!wget -q --show-progress -O data_tutorial/pqk/test_data.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/test_data.csv
!wget -q --show-progress -O data_tutorial/pqk/projections_train.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/projections_train.csv
!wget -q --show-progress -O data_tutorial/pqk/projections_test.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/projections_test.csv
# Check the files have been downloaded
!echo "Dataset files downloaded:"
!ls -lh data_tutorial/pqk/*.csv
args = {
"file_train_data": "train_data.csv",
"file_test_data": "test_data.csv",
"motifs_to_use": ["motif", "motif.1", "motif.2", "motif.3"],
"label_name": "Nalm 6 Cytotoxicity",
"label_binarization_threshold": 0.62,
"filter_for_spacer_motif_third_position": False,
"allow_spacer_motif_last_position": True,
"min_label_value": -1,
"encoder": "one-hot",
}
dir_root = "./"
# Preprocess data
train_data, test_data, train_labels, test_labels, num_class, num_motifs = (
preprocess_data(dir_root=dir_root, args=args)
)
# Encode the data
train_data, test_data = data_encoder(
args, train_data, test_data, num_class, num_motifs
)
14:0:15
De asemenea, transformăm setul de date astfel încât să fie reprezentat ca în scopuri de scalare.
# Change 1 to pi/2
angle = np.pi / 2
tmp = pd.DataFrame(train_data).astype("float64")
tmp[tmp == 1] = angle
train_data = tmp.values
tmp = pd.DataFrame(test_data).astype("float64")
tmp[tmp == 1] = angle
test_data = tmp.values
Verificăm dimensiunile și formele seturilor de date de antrenament și de test.
print(train_data.shape, train_labels.shape)
print(test_data.shape, test_labels.shape)
(172, 60) (172,)
(74, 60) (74,)
Pasul 2: Optimizarea problemei pentru execuția pe hardware cuantic
Circuit cuantic
Construim acum harta de caracteristici care înglobează setul nostru de date clasice într-un spațiu de caracteristici de dimensionalitate mai mare. Pentru această încorporare, folosim ZZFeatureMap din Qiskit.
feature_dimension = train_data.shape[1]
reps = 24
insert_barriers = True
entanglement = "pairwise"
# ZZFeatureMap with linear entanglement and a repetition of 2
embed = ZZFeatureMap(
feature_dimension=feature_dimension,
reps=reps,
entanglement=entanglement,
insert_barriers=insert_barriers,
name="ZZFeatureMap",
)
embed.decompose().draw(output="mpl", style="iqp", fold=-1)

O altă opțiune de încorporare cuantică este ansatz-ul de evoluție a hamiltonianului Heisenberg 1D. Poți sări peste rularea acestei secțiuni dacă dorești să continui cu ZZFeatureMap.
feature_dimension = train_data.shape[1]
num_qubits = feature_dimension + 1
embed2 = QuantumCircuit(num_qubits)
num_trotter_steps = 6
pv_length = feature_dimension * num_trotter_steps
pv = ParameterVector("theta", pv_length)
# Add Haar random single qubit unitary to each qubit as initial state
np.random.seed(42)
seeds_unitary = np.random.randint(0, 100, num_qubits)
for i in range(num_qubits):
rand_gate = UnitaryGate(random_unitary(2, seed=seeds_unitary[i]))
embed2.append(rand_gate, [i])
def trotter_circ(feature_dimension, num_trotter_steps):
num_qubits = feature_dimension + 1
circ = QuantumCircuit(num_qubits)
# Even
for i in range(0, feature_dimension, 2):
circ.rzz(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(0, feature_dimension, 2):
circ.rxx(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(0, feature_dimension, 2):
circ.ryy(2 * pv[i] / num_trotter_steps, i, i + 1)
# Odd
for i in range(1, feature_dimension, 2):
circ.rzz(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(1, feature_dimension, 2):
circ.rxx(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(1, feature_dimension, 2):
circ.ryy(2 * pv[i] / num_trotter_steps, i, i + 1)
return circ
# Hamiltonian evolution ansatz
for step in range(num_trotter_steps):
circ = trotter_circ(feature_dimension, num_trotter_steps)
if step % 2 == 0:
embed2 = embed2.compose(circ)
else:
reverse_circ = circ.reverse_ops()
embed2 = embed2.compose(reverse_circ)
embed2.draw(output="mpl", style="iqp", fold=-1)
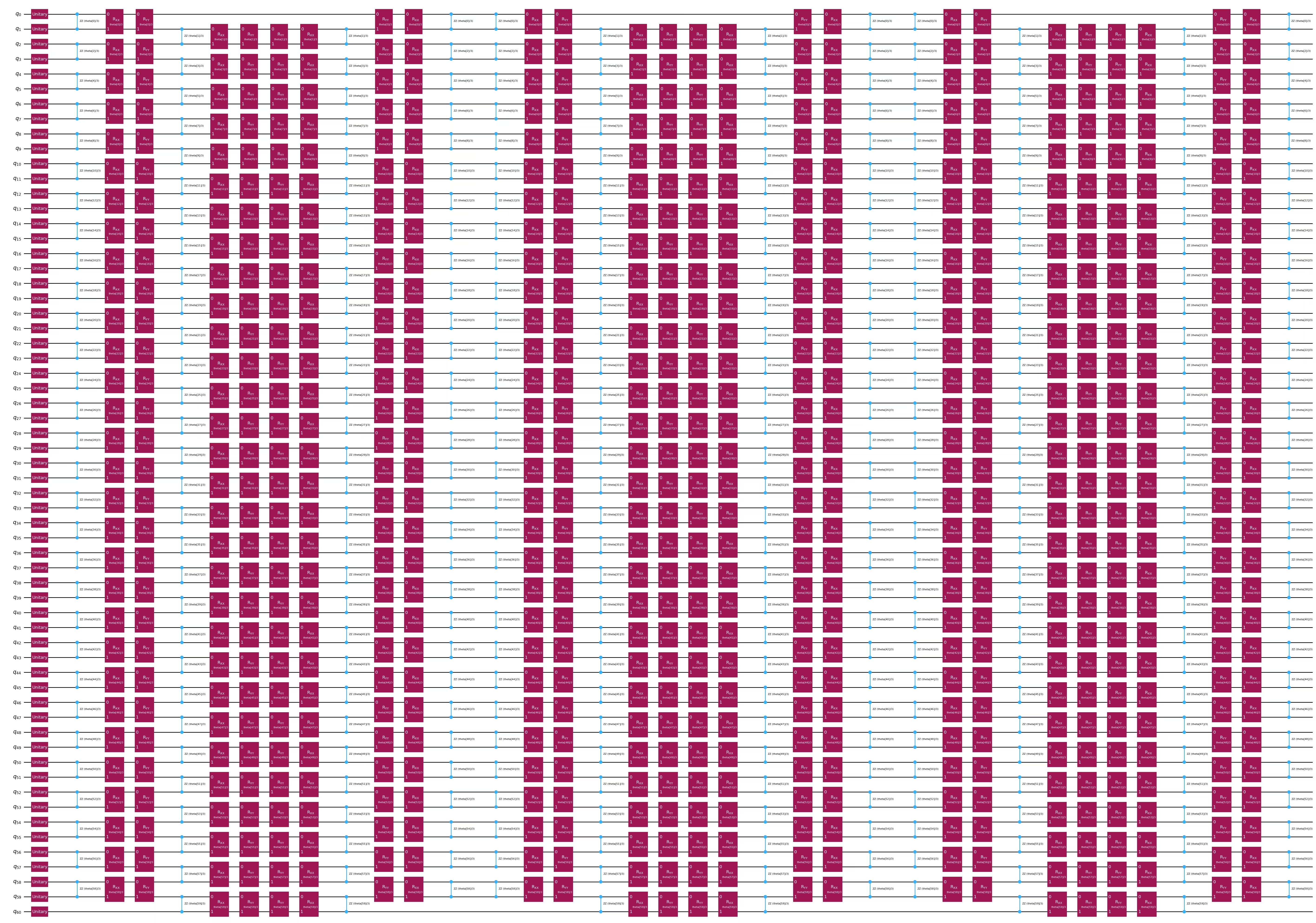
Pasul 3: Execuție folosind primitivele Qiskit
Măsurarea 1-RDM-urilor
Principalele componente ale nucleelor cuantice proiectate sunt matricele de densitate redusă (RDM), obținute prin măsurători proiective ale hărții de caracteristici cuantice. În acest pas, obținem toate matricele de densitate redusă pe un singur qubit (1-RDM), care vor fi furnizate ulterior funcției clasice de nucleu exponențial.
Să vedem cum se calculează 1-RDM pentru un singur punct de date din set, înainte de a itera peste toate datele. 1-RDM-urile sunt o colecție de măsurători pe un singur Qubit ale operatorilor Pauli X, Y și Z pe toți qubiții. Aceasta deoarece o RDM pe un singur Qubit poate fi exprimată complet ca:
Mai întâi selectăm Backend-ul de utilizat.
service = QiskitRuntimeService()
backend = service.least_busy(
operational=True, simulator=False, min_num_qubits=133
)
target = backend.target
Apoi rulăm circuitul cuantic și măsurăm proiecțiile. Rețineți că activăm atenuarea erorilor, inclusiv Extrapolarea Zgomotului Zero (ZNE).
# Let's select the ZZFeatureMap embedding for this example
qc = embed
num_qubits = feature_dimension
# Identity operator on all qubits
id = "I" * num_qubits
# Let's select the first training datapoint as an example
parameters = train_data[0]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(optimization_level=3, target=target)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(mode=backend, options=experimental_opts)
job = estimator.run([pub_x, pub_y, pub_z])
Acum recuperăm rezultatele.
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
print(job_result_x)
print(job_result_y)
print(job_result_z)
[ 3.67865951e-03 1.01158571e-02 -3.95790878e-02 6.33984326e-03
1.86035759e-02 -2.91533268e-02 -1.06374793e-01 4.48873518e-18
4.70201764e-02 3.53997968e-02 2.53130819e-02 3.23903401e-02
6.06327843e-03 1.16313667e-02 -1.12387504e-02 -3.18457725e-02
-4.16445718e-04 -1.45609602e-03 -4.21737114e-01 2.83705669e-02
6.91332890e-03 -7.45363001e-02 -1.20139326e-02 -8.85566135e-02
-3.22648394e-02 -3.24228074e-02 6.20431299e-04 3.04225434e-03
5.72795792e-03 1.11288428e-02 1.50395861e-01 9.18380197e-02
1.02553163e-01 2.98312847e-02 -3.30298912e-01 -1.13979648e-01
4.49159340e-03 8.63861493e-02 3.05666566e-02 2.21463145e-04
1.45946735e-02 8.54537275e-03 -8.09805979e-02 -2.92608104e-02
-3.91243644e-02 -3.96632760e-02 -1.41187613e-01 -1.07363243e-01
1.81089440e-02 2.70778895e-02 1.45139414e-02 2.99480458e-02
4.99137134e-02 7.08789852e-02 4.30565759e-02 8.71287156e-02
1.04334798e-01 7.72191962e-02 7.10059720e-02 1.04650403e-01]
[-7.31765102e-05 7.42669174e-03 9.82277344e-03 5.92638249e-02
4.24120486e-02 -9.06473416e-03 4.55057675e-03 8.43494094e-03
6.92097339e-02 -6.82234424e-02 6.13509008e-02 3.94200491e-02
-1.24037979e-02 1.01976642e-01 7.90538600e-03 -7.19726160e-02
-1.19501703e-16 -1.03796614e-02 7.37382463e-02 1.97238568e-01
-3.59250635e-02 -2.67554009e-02 3.55010633e-02 7.68877990e-02
6.50677589e-05 -6.59298767e-03 -1.23719487e-02 -6.41938151e-02
1.95603072e-02 -2.48448551e-02 5.17784810e-02 -5.93767100e-02
3.11897681e-02 -3.91959720e-18 -4.47769148e-03 1.39202197e-01
-6.56387523e-02 -5.85665483e-02 9.52905894e-03 -8.61460731e-02
3.91790656e-02 -1.27544375e-01 1.63712244e-01 3.36816934e-04
2.26230028e-02 -2.45023393e-05 4.95635588e-03 1.44779564e-01
3.71625177e-02 3.65675948e-03 2.83694017e-02 -7.10500602e-02
-1.15467702e-01 6.21712129e-03 -4.80958959e-02 2.21021066e-02
7.99062499e-02 -1.87164076e-02 -3.67100369e-02 -2.38923731e-02]
[ 6.85871605e-01 5.07725024e-01 8.71024642e-03 3.34823455e-02
4.58684961e-02 9.44384189e-17 -4.46829296e-02 -2.91296778e-02
4.15466461e-02 2.89628330e-02 1.88624017e-03 5.37110446e-02
2.59579053e-03 1.39327071e-02 -2.90781778e-02 5.07209866e-03
5.83403000e-02 2.60764440e-02 4.45999706e-17 -6.66701417e-03
3.03215873e-01 2.26172533e-02 2.43105960e-02 4.98861041e-18
-2.45530791e-02 6.26940708e-02 1.21058073e-02 2.76675948e-04
2.63980996e-02 2.58302364e-02 7.47856723e-02 8.42728943e-02
5.70989097e-02 6.92955086e-02 -5.68313712e-03 1.32199452e-01
8.90511238e-02 -3.45204621e-02 -1.05445836e-01 6.03864150e-03
2.16291384e-02 8.22303162e-03 1.00856715e-02 6.28973151e-02
6.26727169e-02 6.15399206e-02 9.67320897e-02 1.03045269e-16
1.79688783e-01 -1.59960520e-02 -1.15422952e-02 9.60200470e-03
6.58396672e-02 7.78329830e-03 6.53226955e-02 2.45778685e-03
4.36694753e-03 5.75098762e-03 -2.48896201e-02 8.33740755e-05]
Afișăm dimensiunea circuitului și adâncimea porților cu doi qubiți.
print(f"qubits: {qc.num_qubits}")
print(
f"2q-depth: {transpiled_circuit.depth(lambda x: x.operation.num_qubits==2)}"
)
print(
f"2q-size: {transpiled_circuit.size(lambda x: x.operation.num_qubits==2)}"
)
print(f"Operator counts: {transpiled_circuit.count_ops()}")
transpiled_circuit.draw("mpl", fold=-1, style="clifford", idle_wires=False)
qubits: 60
2q-depth: 64
2q-size: 1888
Operator counts: OrderedDict({'rz': 6016, 'sx': 4576, 'cz': 1888, 'x': 896, 'barrier': 31})

Acum putem itera peste întregul set de antrenament pentru a obține toate 1-RDM-urile.
De asemenea, furnizăm rezultatele unui experiment pe care l-am rulat pe hardware cuantic real. Poți fie să rulezi antrenamentul tu însuți setând indicatorul de mai jos la True, fie să folosești rezultatele proiecțiilor pe care le furnizăm noi.
# Set this to True if you want to run the training on hardware
run_experiment = False
# Identity operator on all qubits
id = "I" * num_qubits
# projections_train[i][j][k] will be the expectation value of the j-th Pauli operator (0: X, 1: Y, 2: Z)
# of datapoint i on qubit k
projections_train = []
jobs_train = []
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"return_all_extrapolated": True,
"return_unextrapolated": True,
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
options = EstimatorOptions(experimental=experimental_opts)
if run_experiment:
with Batch(backend=backend):
for i in tqdm.tqdm(
range(len(train_data)), desc="Training data progress"
):
# Get training sample
parameters = train_data[i]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(
optimization_level=3, target=target
)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(options=options)
job = estimator.run([pub_x, pub_y, pub_z])
jobs_train.append(job)
Training data progress: 100%|██████████| 172/172 [13:03<00:00, 4.55s/it]
Odată ce joburile sunt complete, putem recupera rezultatele.
if run_experiment:
for i in tqdm.tqdm(
range(len(train_data)), desc="Retrieving training data results"
):
# Completed job
job = jobs_train[i]
# Job results
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
# Record <X>, <Y> and <Z> on all qubits for the current datapoint
projections_train.append([job_result_x, job_result_y, job_result_z])
Repetăm procesul pentru setul de test.
# Identity operator on all qubits
id = "I" * num_qubits
# projections_test[i][j][k] will be the expectation value of the j-th Pauli operator (0: X, 1: Y, 2: Z)
# of datapoint i on qubit k
projections_test = []
jobs_test = []
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"return_all_extrapolated": True,
"return_unextrapolated": True,
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
options = EstimatorOptions(experimental=experimental_opts)
if run_experiment:
with Batch(backend=backend):
for i in tqdm.tqdm(range(len(test_data)), desc="Test data progress"):
# Get test sample
parameters = test_data[i]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(
optimization_level=3, target=target
)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(options=options)
job = estimator.run([pub_x, pub_y, pub_z])
jobs_test.append(job)
Test data progress: 100%|██████████| 74/74 [00:13<00:00, 5.56it/s]
Putem recupera rezultatele ca mai înainte.
if run_experiment:
for i in tqdm.tqdm(
range(len(test_data)), desc="Retrieving test data results"
):
# Completed job
job = jobs_test[i]
# Job results
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
# Record <X>, <Y> and <Z> on all qubits for the current datapoint
projections_test.append([job_result_x, job_result_y, job_result_z])
Pasul 4: Post-procesare și returnarea rezultatului în formatul clasic dorit
Definirea kernelului cuantic proiectat
Kernelul cuantic proiectat este definit prin următoarea funcție kernel:
În ecuația de mai sus, este un hiperparametru reglabil. reprezintă elementele matricei kernel .
Folosind definiția 1-RDM-urilor, putem observa că termenii individuali din funcția kernel pot fi evaluați ca , unde . Aceste valori de așteptare sunt exact ceea ce am măsurat mai sus.
Prin utilizarea scikit-learn, putem de fapt să calculăm kernelul și mai ușor. Aceasta se datorează kernelului cu funcție de bază radială ('rbf') disponibil imediat: . Mai întâi, trebuie pur și simplu să reformatăm noile seturi de date de antrenare și de test proiectate în tablouri bidimensionale.
Rețineți că parcurgerea întregului set de date poate dura aproximativ 80 de minute pe QPU. Pentru a te asigura că restul tutorialului este ușor de executat, furnizăm suplimentar proiecții dintr-un experiment rulat anterior (care sunt incluse în fișierele descărcate în blocul de cod Download dataset). Dacă ai efectuat antrenarea singur, poți continua tutorialul cu propriile rezultate.
if run_experiment:
projections_train = np.array(projections_train).reshape(
len(projections_train), -1
)
projections_test = np.array(projections_test).reshape(
len(projections_test), -1
)
else:
projections_train = np.loadtxt("projections_train.txt")
projections_test = np.loadtxt("projections_test.txt")
Mașina cu vectori suport (SVM)
Putem acum rula un SVM clasic pe acest kernel precalculat și să folosim kernelul dintre seturile de test și antrenare pentru predicție.
# Range of 'C' and 'gamma' values as SVC hyperparameters
C_range = [0.001, 0.005, 0.007]
C_range.extend([x * 0.01 for x in range(1, 11)])
C_range.extend([x * 0.25 for x in range(1, 60)])
C_range.extend(
[
20,
50,
100,
200,
500,
700,
1000,
1100,
1200,
1300,
1400,
1500,
1700,
2000,
]
)
gamma_range = ["auto", "scale", 0.001, 0.005, 0.007]
gamma_range.extend([x * 0.01 for x in range(1, 11)])
gamma_range.extend([x * 0.25 for x in range(1, 60)])
gamma_range.extend([20, 50, 100])
param_grid = dict(C=C_range, gamma=gamma_range)
# Support vector classifier
svc = SVC(kernel="rbf")
# Define the cross validation
cv = StratifiedKFold(n_splits=10)
# Grid search for hyperparameter tuning (q: quantum)
grid_search_q = GridSearchCV(
svc, param_grid, cv=cv, verbose=1, n_jobs=-1, scoring="f1_weighted"
)
grid_search_q.fit(projections_train, train_labels)
# Best model with best parameters
best_svc_q = grid_search_q.best_estimator_
print(
f"The best parameters are {grid_search_q.best_params_} with a score of {grid_search_q.best_score_:.4f}"
)
# Test accuracy
accuracy_q = best_svc_q.score(projections_test, test_labels)
print(f"Test accuracy with best model: {accuracy_q:.4f}")
Fitting 10 folds for each of 6622 candidates, totalling 66220 fits
The best parameters are {'C': 8.5, 'gamma': 0.01} with a score of 0.6980
Test accuracy with best model: 0.8108
Benchmarking clasic
Putem rula un SVM clasic cu funcția de bază radială ca kernel, fără a efectua o proiecție cuantică. Acest rezultat reprezintă referința noastră clasică.
# Support vector classifier
svc = SVC(kernel="rbf")
# Grid search for hyperparameter tuning (c: classical)
grid_search_c = GridSearchCV(
svc, param_grid, cv=cv, verbose=1, n_jobs=-1, scoring="f1_weighted"
)
grid_search_c.fit(train_data, train_labels)
# Best model with best parameters
best_svc_c = grid_search_c.best_estimator_
print(
f"The best parameters are {grid_search_c.best_params_} with a score of {grid_search_c.best_score_:.4f}"
)
# Test accuracy
accuracy_c = best_svc_c.score(test_data, test_labels)
print(f"Test accuracy with best model: {accuracy_c:.4f}")
Fitting 10 folds for each of 6622 candidates, totalling 66220 fits
The best parameters are {'C': 10.75, 'gamma': 0.04} with a score of 0.7830
Test accuracy with best model: 0.7432
Anexă: Verificarea potențialului avantaj cuantic al setului de date în sarcinile de învățare
Nu toate seturile de date oferă un avantaj potențial din utilizarea PQK-urilor. Există câteva limite teoretice pe care le poți folosi ca test preliminar pentru a vedea dacă un anumit set de date poate beneficia de PQK-uri. Pentru a cuantifica acest lucru, autorii articolului Power of data in quantum machine learning [2] definesc cantități numite complexități ale modelelor clasic și cuantic, respectiv separarea geometrică a modelelor clasic și cuantic. Pentru a anticipa un potențial avantaj cuantic din PQK-uri, separarea geometrică dintre kernelurile clasic și cuantic-proiectat ar trebui să fie aproximativ de ordinul , unde este numărul de eșantioane de antrenare. Dacă această condiție este satisfăcută, trecem la verificarea complexităților modelelor. Dacă complexitatea modelului clasic este de ordinul , în timp ce complexitatea modelului cuantic-proiectat este substanțial mai mică decât , putem anticipa un avantaj potențial din PQK. Separarea geometrică este definită astfel (F19 în [2]):
# Gamma values used in best models above
gamma_c = grid_search_c.best_params_["gamma"]
gamma_q = grid_search_q.best_params_["gamma"]
# Regularization parameter used in the best classical model above
C_c = grid_search_c.best_params_["C"]
l_c = 1 / C_c
# Classical and quantum kernels used above
K_c = rbf_kernel(train_data, train_data, gamma=gamma_c)
K_q = rbf_kernel(projections_train, projections_train, gamma=gamma_q)
# Intermediate matrices in the equation
K_c_sqrt = sqrtm(K_c)
K_q_sqrt = sqrtm(K_q)
K_c_inv = inv(K_c + l_c * np.eye(K_c.shape[0]))
K_multiplication = (
K_q_sqrt @ K_c_sqrt @ K_c_inv @ K_c_inv @ K_c_sqrt @ K_q_sqrt
)
# Geometric separation
norm = np.linalg.norm(K_multiplication, ord=np.inf)
g_cq = np.sqrt(norm)
print(
f"Geometric separation between classical and quantum kernels is {g_cq:.4f}"
)
print(np.sqrt(len(train_data)))
Geometric separation between classical and quantum kernels is 1.5440
13.114877048604
Complexitatea modelului este definită astfel (M1 în [2]):
# Model complexity of the classical kernel
# Number of training data
N = len(train_data)
# Predicted labels
pred_labels = best_svc_c.predict(train_data)
pred_matrix = np.outer(pred_labels, pred_labels)
# Intermediate terms
K_c_inv = inv(K_c + l_c * np.eye(K_c.shape[0]))
# First term
first_sum = np.sum((K_c_inv @ K_c_inv) * pred_matrix)
first_term = l_c * np.sqrt(first_sum / N)
# Second term
second_sum = np.sum((K_c_inv @ K_c @ K_c_inv) * pred_matrix)
second_term = np.sqrt(second_sum / N)
# Model complexity
s_c = first_term + second_term
print(f"Classical model complexity is {s_c:.4f}")
Classical model complexity is 1.3578
# Model complexity of the projected quantum kernel
# Number of training data
N = len(projections_train)
# Predicted labels
pred_labels = best_svc_q.predict(projections_train)
pred_matrix = np.outer(pred_labels, pred_labels)
# Regularization parameter used in the best classical model above
C_q = grid_search_q.best_params_["C"]
l_q = 1 / C_q
# Intermediate terms
K_q_inv = inv(K_q + l_q * np.eye(K_q.shape[0]))
# First term
first_sum = np.sum((K_q_inv @ K_q_inv) * pred_matrix)
first_term = l_q * np.sqrt(first_sum / N)
# Second term
second_sum = np.sum((K_q_inv @ K_q @ K_q_inv) * pred_matrix)
second_term = np.sqrt(second_sum / N)
# Model complexity
s_q = first_term + second_term
print(f"Quantum model complexity is {s_q:.4f}")
Quantum model complexity is 1.5806
Referințe
- Utro, Filippo, et al. "Enhanced Prediction of CAR T-Cell Cytotoxicity with Quantum-Kernel Methods." arXiv preprint arXiv:2507.22710 (2025).
- Huang, Hsin-Yuan, et al. "Power of data in quantum machine learning." Nature communications 12.1 (2021): 2631.
- Daniels, Kyle G., et al. "Decoding CAR T cell phenotype using combinatorial signaling motif libraries and machine learning." Science 378.6625 (2022): 1194-1200.